Os dados epidemiológicos do momento dizem que: SARS-CoV-2 está presente em mais de 200 países do mundo, aproximadamente 113 milhões de pessoas adoeceram com COVID-19 em todo o mundo (fevereiro de 2021) e, destes, não 2,5 milhões faleceu.
O SARS-CoV-2 é um vírus que afeta principalmente o trato respiratório, causando sintomas como tosse, resfriado, febre e, em casos graves, dificuldades respiratórias; às vezes, porém, também pode induzir inflamação sistêmica, causando sepse, insuficiência cardíaca e disfunção de múltiplos órgãos.
A infecção por SARS-CoV-2 é particularmente perigosa para indivíduos com mais de 60 anos, para aqueles com doenças crônicas (por exemplo: diabetes, doença arterial coronariana) e para pessoas em terapia com medicamentos depressores do sistema imunológico (por exemplo: quimioterapia, imunossupressores).
Este artigo tem como objetivo analisar a estrutura, o genoma e as proteínas do SARS-CoV-2, e fornecer informações fundamentais relacionadas à patogênese do vírus.
Para mais informações: SARS-CoV-2: como reconhecer os primeiros sintomas e o que fazer , O SARS-CoV-2 é um vírus de RNA de fita simples positivo com pericapsídeo (ou envelope).
O pericapsídeo é uma espécie de envelope colocado em torno do capsídeo de alguns vírus; é composto de fosfolipídios e glicoproteínas.
O SARS-CoV-2 possui um genoma de 29.881 bases nitrogenadas, que codifica para 9.860 aminoácidos.
Este genoma é dividido em genes para proteínas estruturais e genes para proteínas não estruturais.
Os genes da proteína estrutural codificam a proteína spike (abreviada para S), a proteína pericapsídeo (abreviada para E, do envelope), a proteína de membrana (abreviada para M) e a proteína do nucleocapsídeo (abreviada para N).
Como o nome sugere, as proteínas estruturais se combinam para formar a estrutura do SARS-CoV-2.
Os genes para proteínas não estruturais, por outro lado, codificam proteínas, como a protease semelhante à 3-quimiotripsina, a protease semelhante à papaína ou a RNA polimerase dependente de RNA, cujas funções são regular e direcionar os processos de replicação. E montagem de vírus.
Abaixo está uma descrição das proteínas estruturais individuais, com foco na proteína S, e das proteínas não estruturais.
Você sabia disso ...
O SARS-CoV-2 compartilha aproximadamente 82% de seu genoma com os coronavírus SARS-CoV (responsável pelo SARS) e MERS-CoV (responsável pela síndrome respiratória do Oriente Médio).
Para saber mais: Coronavirus: o que são? a aparência de uma coroa (daí o termo "Coronavírus").
A proteína do pico pesa 180-200 kDa (leia-se kiloDalton) e é composta por 1.273 aminoácidos.
O pico é feito de dois componentes principais de aminoácidos, chamados subunidades S1 (14-685) e subunidades S2 (686-1,273):
- A subunidade S1 hospeda uma sequência de aminoácidos conhecida como RBD (acrônimo em inglês para "Domínio de ligação ao receptor", isto é, domínio de ligação ao receptor), que é essencial para ligar o vírus às células do hospedeiro (ou seja, o ser humano).
- Já a subunidade S2 é o sítio das sequências de aminoácidos (peptídeo de fusão, HR1, HR2, domínio transmembranar e domínio citoplasmático), cuja função final é favorecer a fusão e a entrada do vírus nas células hospedeiras.
Em seu estado nativo (ou seja, quando o vírus não está infectando ninguém), a proteína spike está na forma de um precursor inativo. Quando o vírus encontra um organismo potencial para ser infectado, no entanto, ele muda imediatamente para uma forma ativa: as proteases das células-alvo desencadeiam o processo de ativação (portanto, é o próprio hospedeiro que o ativa!), Que "quebram" "o espigam e formam as subunidades S1 e S2.
Como a proteína de pico SARS-CoV-2 funciona

O funcionamento da proteína spike SARS-CoV-2 é complexo; o artigo em questão visa simplificá-lo ao máximo, para que possa ser compreendido pelos leitores.
A proteína spike é essencial para iniciar o processo de infecção do hospedeiro, ou seja, é a arma que o Novo Coronavírus usa para causar a infecção conhecida como COVID-19.
O processo de infecção impulsionado por picos pode ser dividido em duas fases:
- A ligação à célula hospedeira. É a fase em que o vírus ataca e se liga às células do organismo que irá infectar.
- A fusão da membrana viral (essencialmente do vírus) com a membrana da célula hospedeira. É a fase que permite ao vírus entrar nas células do organismo atacado e aí disseminar seu genoma.
Ligação às células hospedeiras
A proteína spike liga-se às células hospedeiras através da sequência RBD da subunidade S1.
Estudos científicos observaram que a sequência RBD se liga às células hospedeiras por meio de uma "interação com o receptor ACE2 colocado na superfície da membrana plasmática das próprias células.
A ACE2 é uma enzima homóloga da ACE, a proteína responsável pela conversão da angiotensina 1-9.
Em humanos, a ECA2 é encontrada principalmente na superfície da membrana plasmática das células de órgãos como pulmões, intestinos, coração e rins.
Uma vez que a subunidade S1 é ligada a ACE2, a proteína S começa a mudar de conformação; este evento serve para favorecer a fase de fusão e a entrada do vírus na célula hospedeira.
A ligação à ACE2 e a alteração conformacional resultante são dois aspectos fundamentais para a realização da vacina contra a SARS-CoV-2 e para o entendimento dos mecanismos de antigenicidade e resposta imune implementados pelo hospedeiro.
No entanto, há um problema que deve ser considerado: mutações na subunidade S1 e, em particular na sequência RBD, podem alterar a forma como a alteração conformacional se desenvolve; consequentemente, isso pode afetar as características antigênicas e vacinas de eficácia (aprender mais sobre o assunto, recomendamos a leitura do artigo dedicado às variantes do SARS-CoV-2).
Fusão de célula hospedeira
A proteína spike funde o vírus à célula hospedeira por meio das sequências de aminoácidos da subunidade S2.
O processo de fusão do vírus ocorre na onda da mudança conformacional da proteína S induzida pela ligação entre RBD e o receptor ACE2 do hospedeiro: a mudança na conformação do pico, de fato, aproxima a membrana viral da membrana plasmática da célula hospedeira. , até à interação, à fusão entre membranas e, por fim, à incorporação do vírus infectante.
Uma vez que o genoma viral está dentro da célula hospedeira, o vírus começa sua replicação e o processo de infecção pode ser considerado completo.
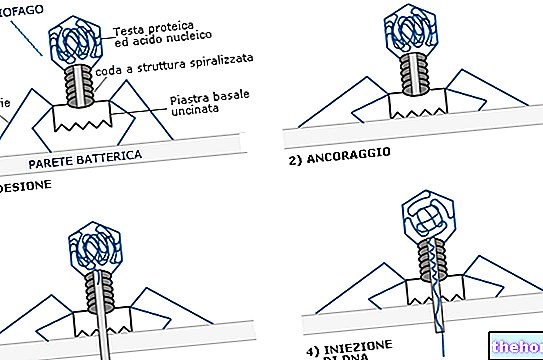
Para mais informações: Mutações de proteína de pico: Variantes SARS-CoV-2 maduro, com seu ácido nucléico (DNA ou RNA) encerrado em uma cápsula de proteína, chamada capsídeo.Os estudos a esse respeito mostraram que a proteína E SARS-CoV-2 é uma viroporina que, uma vez na célula hospedeira, vai se localizar na membrana do aparelho de Golgi e do retículo endoplasmático, para facilitar a montagem e liberação de vírions.
A viroporina é uma proteína viral que atua como um canal de membrana dentro das células do hospedeiro.
A proteína E SARS-CoV-2 é muito semelhante à do SARS-CoV, embora tenha algumas diferenças em relação ao MERS-CoV.
viral, denominada proteases e produzida precocemente pelo vírus; essas proteases se encarregam de "cortar" as poliproteínas em pontos precisos, para dar origem às proteínas não estruturais únicas.
A estratégia de poliproteína (da qual derivam proteínas menores) é muito comum entre os vírus.
É interessante ressaltar que, antes do trabalho de corte, as proteínas ainda incluídas nas poliproteínas são inativas, não funcionais, só se tornam funcionais após a intervenção das proteases e sua clivagem em relação às principais cadeias de aminoácidos.
A principal função das proteínas não estruturais SARS-CoV-2 é lidar com a transcrição e replicação do RNA viral.
No entanto, deve-se observar que essas proteínas também estão envolvidas na patogênese viral.
Protease SARS-CoV-2
Duas proteínas não estruturais fundamentais para o SARS-CoV-2 são, sem dúvida, as proteases que tratam de "cortar" as poliproteínas e formar as proteínas úteis para a transcrição e replicação do RNA viral.
Essas proteases são conhecidas como proteases semelhantes à 3-quimotripsina (abreviada para 3CLpro) e proteases semelhantes à papaína (abreviada para PLpro).
Considerando que as proteínas por elas originadas servem para disseminar a infecção no hospedeiro, as proteases em questão representam um interessante alvo farmacológico.
RNA polimerase dependente de RNA
A RNA polimerase dependente de RNA é a proteína não estrutural do SARS-CoV-2 essencial para a replicação do genoma viral destinada a novos vírions.
Esta proteína não estrutural também representaria um alvo farmacológico atraente.
do hospedeiro e os explora para traduzir seu próprio genoma em RNA e criar as proteínas necessárias para a replicação do mesmo material genético e para a montagem de novos vírions.Com base no acima exposto, um papel fundamental na transcrição e replicação do RNA viral pertence às proteínas não estruturais.
Com a transcrição e replicação do genoma viral, o SARS-CoV-2 começa a se espalhar no hospedeiro, dando início à própria doença infecciosa.
Nesta fase, o vírus atua no organismo hospedeiro tanto com atividade citocida (ou seja, que mata as células), quanto com mecanismos imunomediados.
No que diz respeito à atividade citocida, a evidência sugere que o SARS-CoV-2 induz apoptose (morte celular) e lise celular; mais especificamente, descobriu-se que o vírus produz sincícios dentro da célula infectada e causa ruptura celular. "Aparelho de Golgi. , após a replicação.
Quanto aos mecanismos imunomediados, a pesquisa mostrou que o SARS-CoV-2 envolve tanto o sistema imune inato quanto o adaptativo (anticorpos e linfócitos T).
Por que o SARS-CoV-2 é mais infeccioso do que o SARS Coronavirus?
O SARS-CoV, o coronavírus responsável pelo SARS, também invade as células hospedeiras, explorando a interação entre o RBD e o receptor ACE2 presente nas células do trato respiratório.
No entanto, há uma diferença importante entre esse tipo de ligação e aquela colocada pelo SARS-CoV-2: a sequência RBD do Coronavírus responsável pelo COVID-19 tem muito mais afinidade para a ACE2 e se liga a ela com muito mais eficiência. , resultando muito mais eficaz no processo de invasão das células hospedeiras.
Estudos científicos a esse respeito mostraram que a diferença na interação descrita acima se deve a uma composição diferente de aminoácidos entre RBD de SARS-CoV e RBD de SARS-CoV-2; em particular, existem duas regiões de aminoácidos com diferenças importantes.
Essa diferença de afinidade explica vários aspectos:
- A razão pela qual o SARS-CoV-2 tem um R0 mais alto do que o SARS-CoV;
- A razão pela qual os medicamentos e vacinas que visam a sequência RBD do SARS-CoV e parecem ser eficazes não são adequados contra o SARS-CoV-2.
O que é R0?
Também conhecido como "número de reprodução de base", R0 representa o número médio de infecções secundárias produzidas por cada indivíduo infectado em uma população totalmente suscetível (ou seja, nunca em contato com o novo patógeno emergente).
Este parâmetro mede a transmissibilidade potencial de uma doença infecciosa.
As citocinas pró-inflamatórias surgem da atividade de certas células do sistema imunológico.
Em condições normais, servem para regular a resposta imunológica, inflamação e hematopoiese.
Além disso, dados clínicos e outras pesquisas mostraram que a superprodução de citocinas pró-inflamatórias observada na presença de uma infecção grave de SARS-CoV-2 pode se espalhar para outros órgãos (por exemplo, o coração), causando disfunções e afetando a coagulação processos, induzindo a formação de trombo.
Quando o SARS-CoV-2 desencadeia uma extensa superprodução de citocinas pró-inflamatórias, os especialistas referem-se ao fenômeno como "síndrome da tempestade de citocinas".



-quali-sono-e-malattie-associate.jpg)